Originalmente, se pensaba que eran solo motas de polvo en un portaobjetos microscópico.
Ahora, un nuevo estudio sugiere que los microcromosomas, un tipo de cromosoma pequeño que se encuentra en aves y reptiles, tienen una historia más larga y un papel más importante que desempeñar en los mamíferos de lo que podríamos haber anticipado.
Al alinear las secuencias de ADN de cromosomas precisos en muchas especies diferentes, los investigadores pudieron mostrar la consistencia de estas moléculas de ADN en familias de aves y reptiles, una consistencia que se remonta a cientos de millones de años.
Además, el equipo descubrió que estos fragmentos de código genético se barajaron y colocaron en cromosomas más grandes en mamíferos marsupiales y placentarios, incluidos los humanos. En otras palabras, el genoma humano no es tan «normal» como se suponía anteriormente.
«Hemos clasificado y comparado estas secuencias de aves, tortugas, serpientes, lagartijas, ornitorrincos y humanos». La genetista Jenny Graves dice:de la Universidad La Trobe, Australia. “Sorprendentemente, los cromosomas exactos eran similares en todas las especies de aves y reptiles.
«Y lo más sorprendente, eran los mismos pequeños cromosomas de amphioxus, un pequeño animal parecido a un pez sin columna vertebral que fue el último ancestro común con los vertebrados hace 684 millones de años».
Al rastrear estos diminutos cromosomas hasta los antiguos anfioxo, los científicos pudieron establecer vínculos genéticos para todos sus descendientes. Estas pequeñas motas de polvo son en realidad bloques de construcción importantes para los vertebrados, no solo aditivos no naturales.
La mayoría de los mamíferos parecen haber absorbido y mezclado sus microcromosomas durante su evolución, haciéndolos parecer piezas normales de ADN. La excepción es el ornitorrinco, que tiene muchas secciones cromosómicas que se alinean con cromosomas finos, lo que sugiere que este método puede servir como un «trampolín» para otros mamíferos en este sentido, según los investigadores.
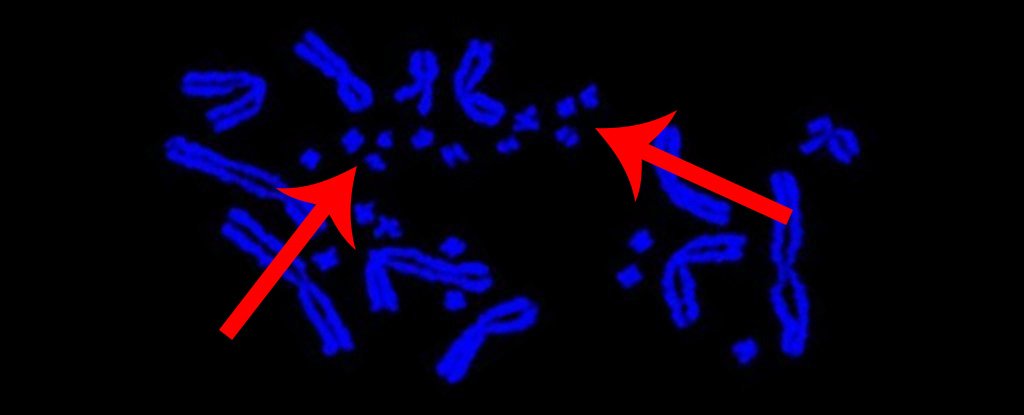
Los cromosomas diminutos son consistentes en aves y reptiles, pero se mezclan con los cromosomas más grandes en mamíferos. (Paul Waters)
El estudio también reveló que, además de ser similares en muchas especies, los microcromosomas también estaban ubicados en la misma ubicación dentro de las células.
«No solo son similares en cada tipo, sino que están agrupados en el centro del núcleo donde interactúan físicamente entre sí, lo que indica coherencia funcional». El biólogo Paul Waters dice:de la Universidad de Nueva Gales del Sur (UNSW) en Australia.
«Este comportamiento extraño no es cierto para los cromosomas grandes de nuestros genomas».
Los investigadores atribuyen los avances recientes en la tecnología de secuenciación de ADN a la capacidad de secuenciar cromosomas precisos de un extremo a otro, determinando dónde y con qué propósito aparecen estos fragmentos de ADN.
No está claro si existe un beneficio evolutivo de codificar el ADN en cromosomas más grandes o en cromosomas diminutos, y los hallazgos descritos en este documento pueden ayudar a los científicos a poner fin a este debate en particular, aunque quedan muchas preguntas.
El estudio sugiere que el enfoque de cromosomas grandes que se originó en los mamíferos no es en realidad la norma y puede ser un defecto: los genes están estrechamente empaquetados en microcromosomas, por ejemplo.
En lugar de ser «normales», los cromosomas de los humanos y otros mamíferos estaban llenos de una gran cantidad de «ADN basura» y se mezclaban de muchas formas diferentes. Graves dice.
«El nuevo conocimiento ayuda a explicar por qué hay un grupo tan grande de mamíferos con genomas completamente diferentes que habitan en cada rincón de nuestro planeta».
La búsqueda fue publicada en PNAS.

«Solucionador de problemas. Gurú de los zombis. Entusiasta de Internet. Defensor de los viajes sin disculpas. Organizador. Lector. Aficionado al alcohol».