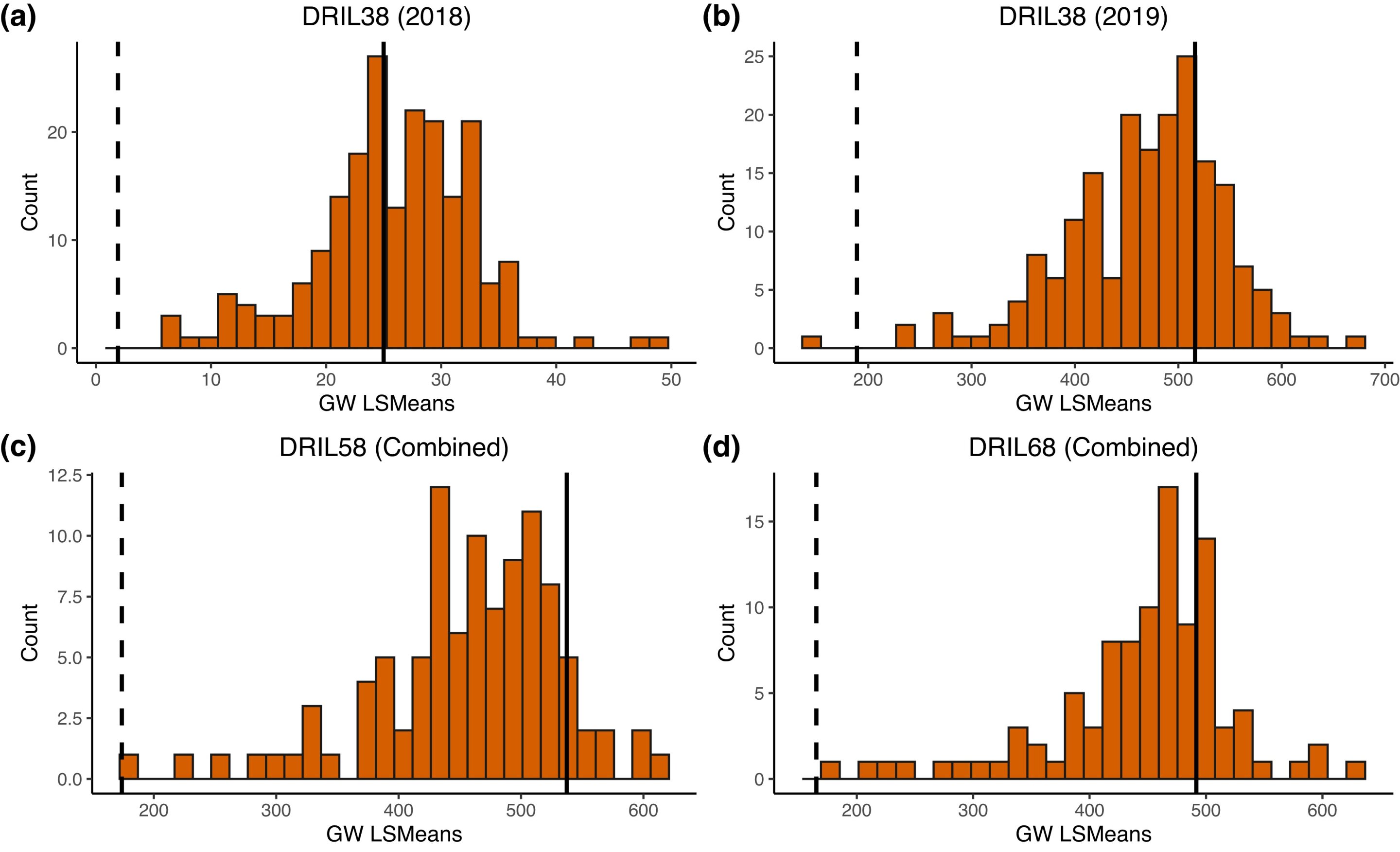
Distribución fenotípica de GW en las tres poblaciones. Para los conjuntos DRIL58 y DRIL68, se muestran estimaciones de LsMeans para el entorno combinado de AUDPC para los datos de GW. Para el grupo DRIL38, solo hubo una clasificación en 2018 y no se calculó el ABCP. Por lo tanto, la distribución de la estimación DRIL38 de 2018 no se combinó con la estimación DRIL38 de 2019, que se basó en el AUDPC calculado utilizando 3 evaluaciones. La línea sólida indica las LsMedias del padre recurrente compartido Oh7B y las líneas discontinuas indican las LsMedias de los padres donantes, que varían para cada población. La línea donante para la población DRIL38 es Ki3; Para la población DRIL58 es NC262 y para la población DRIL68 es NC304. crédito: G3: Genes, Genomas, Genética (2023). doi: 10.1093/g3journal/jkad275
× Cerca
Distribución fenotípica de GW en las tres poblaciones. Para los conjuntos DRIL58 y DRIL68, se muestran estimaciones de LsMeans para el entorno combinado de AUDPC para los datos de GW. Para el grupo DRIL38, solo hubo una clasificación en 2018 y no se calculó el ABCP. Por lo tanto, la distribución de la estimación DRIL38 de 2018 no se combinó con la estimación DRIL38 de 2019, que se basó en el AUDPC calculado utilizando 3 evaluaciones. La línea sólida indica las LsMedias del padre recurrente compartido Oh7B y las líneas discontinuas indican las LsMedias de los padres donantes, que varían para cada población. La línea donante para la población DRIL38 es Ki3; Para la población DRIL58 es NC262 y para la población DRIL68 es NC304. crédito: G3: Genes, Genomas, Genética (2023). doi: 10.1093/g3journal/jkad275
En un clima cambiante, los productores de maíz deben estar preparados para cualquier cosa, incluidas las dinámicas de enfermedades nuevas y cambiantes. Dado que es imposible predecir qué enfermedades dañinas aparecerán en un año determinado, el maíz resistente a múltiples enfermedades sería una gran victoria para los agricultores. Ahora, investigadores de la Universidad de Illinois Urbana-Champaign están trabajando para acercar a la industria a ese objetivo.
El marchitamiento del ganso, una enfermedad bacteriana, las enfermedades fúngicas, la mancha gris de la hoja, el tizón de la hoja del maíz del norte y el tizón de la hoja del maíz del sur son importantes para los productores de todo el medio oeste de los Estados Unidos y, en algunos casos, a nivel mundial. El estudio publicado en G3: Genes, Genomas, GenéticaRevela regiones genómicas asociadas con la resistencia a las cuatro enfermedades.
«No sólo encontramos regiones del genoma que confieren resistencia a cada enfermedad, sino que también identificamos un conjunto de líneas experimentales de maíz que eran resistentes a todas estas enfermedades», dijo Tiffany. «Estos hallazgos deberían ayudar a la industria a desarrollar materiales que son resistentes a múltiples enfermedades a la vez”. Jamann, autor principal del nuevo estudio y profesor asociado en el Departamento de Ciencias de los Cultivos, parte de la Facultad de Ciencias Agrícolas, del Consumidor y Ambientales (ACES) de la U of I.
El equipo realizó varios cruces estratégicos entre líneas de maíz resistentes y susceptibles a enfermedades, lo que les permitió mapear rasgos de resistencia en ubicaciones específicas del genoma. Actualmente, estas regiones son bastante grandes y comprenden cientos de genes individuales. Si existen genes específicos con efectos significativos, aún no se han identificado.
Sin embargo, identificar regiones importantes es útil, ya que la resistencia a las enfermedades rara vez está vinculada a un solo gen. De hecho, la fuerza agregada o cuantitativa de múltiples genes trabajando juntos podría significar una resistencia más sostenida. Existe un respaldo si el patógeno encuentra una manera de sortear un mecanismo de resistencia particular. Curiosamente, esta solidez también puede funcionar contra diferentes grupos de patógenos.
«Encontramos 19 regiones asociadas con la resistencia a la marchitez bacteriana de Goss. Muchas de estas regiones también están implicadas en la resistencia a los hongos patógenos», dijo Gaman. «Por lo tanto, es posible generar resistencia a varias enfermedades simultáneamente utilizando las mismas regiones genéticas».
Los hongos y las bacterias son muy diferentes biológicamente, pero ambos deben encontrar formas de llegar a la planta, viajar alrededor de ella y reproducirse. Es posible que los genes de resistencia desencadenen cambios en la vasculatura de una planta para dificultar el desplazamiento de ambos tipos de patógenos, dice Gaman, pero todavía no puede determinar exactamente cómo los genes ayudan a las plantas a protegerse. Sin embargo, está trabajando en ello gracias a una subvención de 2022 de la Fundación Nacional de Ciencias.
Aunque el equipo ha identificado tres líneas de maíz resistentes a las cuatro enfermedades, pasará algún tiempo antes de que los agricultores puedan comprar semillas de maíz resistentes a múltiples enfermedades como resultado de este trabajo. Primero, el equipo de Gaman mapeará cuidadosamente las regiones resaltadas en este estudio para encontrar genes que tengan un efecto significativo y luego transmitirá esta información a los criadores que puedan desarrollar nuevos híbridos poderosos. Sin embargo, dice Jaman, se avecinan múltiples resistencias.
más información:
Yuting Qiu et al., Identificación de loci que confieren resistencia a cuatro enfermedades foliares en el maíz, G3: Genes, Genomas, Genética (2023). doi: 10.1093/g3journal/jkad275

«Solucionador de problemas. Gurú de los zombis. Entusiasta de Internet. Defensor de los viajes sin disculpas. Organizador. Lector. Aficionado al alcohol».