crédito: Proteínas: estructura, función y bioinformática. (2023). doi: 10.1002/prot.26496
× Cerca
crédito: Proteínas: estructura, función y bioinformática. (2023). doi: 10.1002/prot.26496
Cuando los profesores. A Joel Sussman e Israel Sillman se les pidió que asesoraran a estudiantes chinos en línea durante la pandemia de COVID-19, y lo último que esperaban de esta experiencia era una investigación altamente innovadora sobre la evolución de las proteínas que podría cambiar nuestra comprensión de la forma en que surgen nuevas proteínas. .
«Al principio era escéptico», recuerda Sussman. «Todos eran estudiantes universitarios y comunicarse a través de una pantalla de computadora no era muy prometedor». Pero él y Silman (dos profesores del Instituto Weizmann de Ciencias con cientos de estudios conjuntos sobre la estructura y función de las proteínas) acordaron impartir tutorías para un equipo de cuatro estudiantes de las principales universidades de China. La tutoría en línea formó parte del programa YutChun-Weizmann, dirigido por el profesor Pinghai Yan de Weizmann.
Sussman y Sillman pidieron a los estudiantes que se dirigieran a ellos por su nombre de pila, una práctica nunca antes vista en las universidades chinas, y los animaron a desarrollar el pensamiento crítico. Sin embargo, no esperaban más que un resumen respetable cuando pidieron a los estudiantes que revisaran sus antiguas investigaciones sobre variaciones de secuencias de proteínas. En cambio, los estudiantes regresaron con una crítica profunda, analizando el estudio desde una perspectiva contemporánea y sugiriendo que algunas de sus conclusiones podrían revisarse utilizando nuevos métodos.
Jing Liu, una de los cuatro alumnos, dice que para ella y los demás estudiantes, esto fue un cambio radical de lo que estaban acostumbrados. «En China, un estudiante que estudia, por ejemplo, una maestría no puede desafiar a un candidato a doctorado o a un investigador postdoctoral; podría enfadarse o decírselo al investigador principal», explica. Sin embargo, se apresuró a señalar que el ambiente era diferente en el campus del Instituto Tecnológico Technion-Israel en Guangdong, donde ella estudiaba en ese momento. “Tenía un supervisor que estaba dispuesto a escucharme y conversar, algo difícil de encontrar en otras universidades de China”.
Las clases en línea, para sorpresa de ambas partes, rápidamente se convirtieron en discusiones. Un estudio realizado en 2017 por científicos checos, que Liu llamó la atención de sus profesores, se convirtió en un tema importante de deliberación, que insinuaba un desarrollo interesante en la historia de la evolución de las proteínas.
Muescas en el nódulo plegable.
A medida que los organismos unicelulares que alguna vez habitaron la Tierra evolucionan hacia organismos más complejos, los cambios ocasionales en su ADN, si dichos cambios son beneficiosos, tienden a preservarse, gracias a la selección natural, y transmitirse a organismos superiores. Es por eso que la mayoría de los genes que codifican proteínas en nuestro cuerpo tienen equivalentes (el término científico es «homólogos») en muchas otras especies a lo largo del árbol evolutivo, hasta las levaduras o las bacterias. A medida que las proteínas evolucionaron, muchas de ellas comenzaron a plegarse en estructuras complejas que les permitieron realizar tareas especializadas.
Dado que la selección natural ha estado operando durante miles de millones de años, parece que las proteínas han tenido tiempo suficiente para evolucionar todas las secuencias beneficiosas posibles. De hecho, hasta hace poco, los científicos creían que todas las proteínas existentes nacían mejorando las secuencias existentes, y que hacía mucho tiempo que no aparecían verdaderas proteínas nuevas.
Pero hace poco más de una década, comenzaron a aparecer grietas en este evangelio científico: surgió evidencia de que siguen surgiendo nuevas proteínas todo el tiempo. A medida que los científicos comenzaron a secuenciar los genomas completos de varios organismos, las comparaciones revelaron la presencia de genes que codifican proteínas «recién nacidas» en todas las especies, desde bacterias hasta humanos. Se cree que estas proteínas se originan en regiones no codificantes que constituyen la mayor parte del genoma. En este escenario, un tramo de ADN que carece de una receta para proteínas adquiere por casualidad una serie de mutaciones que lo convierten en un gen codificador de proteínas.
El estudio checo, que intrigó a Liu y sus profesores, abrió una grieta adicional en la doctrina. Los investigadores checos crearon alrededor de 100 secuencias de proteínas hipotéticas mezclando aleatoriamente genes de proteínas existentes como si fueran una baraja de cartas. Cuando sintetizaron estas proteínas «nunca nacidas» y las probaron en el laboratorio, descubrieron que alrededor de un tercio de ellas mostraban signos de plegamiento en estructuras compactas, como las proteínas naturales.
«Esto fue absolutamente asombroso», dice Sussman. «Si alguien me hubiera preguntado alguna vez si era posible plegar una secuencia de proteínas aleatoria de esta manera, habría dicho que nunca».
Sillman explica que la capacidad de las proteínas para plegarse es esencial para la vida. Aunque no todas las proteínas se pliegan, son las proteínas plegadas, con segmentos organizados, las que realizan funciones catalíticas críticas en los organismos vivos. Al demostrar que las proteínas «que nunca nacen» pueden plegarse, el estudio checo indicó que no sólo podrían nacer nuevas proteínas, sino que también podrían desempeñar nuevas funciones biológicas.
huérfanos nacidos
¿Cómo se convierte un trozo de ADN no codificante en una proteína «recién nacida» y cómo se activa esta proteína? ¿Cuál es la escala de tiempo para estos procesos? ¿Podrían algún día explotarse los mecanismos implicados en el diseño de proteínas?
Para ayudar a responder estas preguntas, Sussman y Sillman decidieron realizar lo que se convirtió, hasta donde sabían, en uno de los primeros estudios estructurales de proteínas nacientes. Lanzaron el proyecto con Liu, el primer autor del artículo, y Rong Qingyuan, entonces estudiante de la Universidad Tsinghua en Beijing. Los cuatro se conocieron online durante un año y medio antes de completar su búsqueda. publicado Recientemente en la revista Proteínas: estructura, función y bioinformática.. Los otros dos estudiantes, Wei Shao y Jitong Wang, participaron en las primeras etapas del proyecto; Abandonó el estudio al final del programa educativo programado, pero son coautores del artículo publicado.
El equipo exploró la posibilidad de plegar proteínas «nacientes» con la ayuda de herramientas de inteligencia artificial (IA) que han revolucionado el estudio de las estructuras de las proteínas en los últimos años. Estos algoritmos ahora pueden, en la mayoría de los casos, predecir de manera confiable la estructura 3D de una proteína basándose únicamente en su secuencia de aminoácidos, evitando la necesidad de cultivar cristales de proteínas y determinar su estructura experimentalmente.
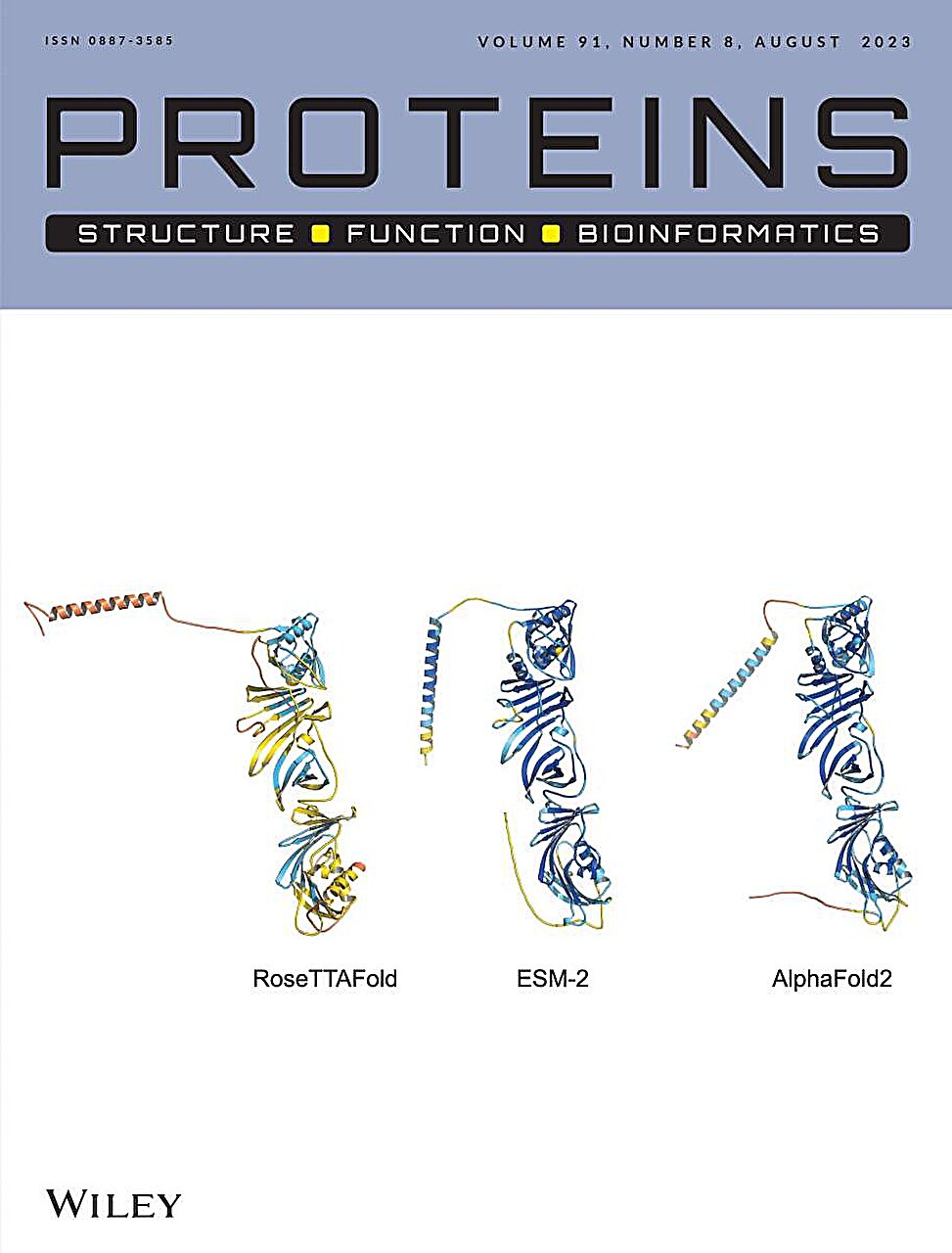
Uno de los principales desafíos que enfrentó el equipo fue que estos algoritmos de predicción funcionan mejor cuando la proteína de interés tiene muchos homólogos (equivalentes de otras especies), mientras que las proteínas «recién generadas», por definición, están presentes en sólo una o un puñado de proteínas. . Clasificar. Debido a que no tienen padres evolutivos, a veces se las denomina proteínas huérfanas (o proteínas cuasi huérfanas, si existen sólo en unas pocas especies relacionadas). Se necesitó la experiencia del equipo para aplicar con éxito herramientas de IA a proteínas huérfanas menos homogéneas. Para aumentar las posibilidades de obtener resultados fiables, los científicos utilizaron tres algoritmos de inteligencia artificial diferentes (AlphaFold2, RoseTTAFold y ESMFold) y compararon sus resultados.
Primero, el equipo utilizó los tres algoritmos para predecir las estructuras 3D de las secuencias de proteínas híbridas «nunca generadas» del estudio checo. Las predicciones identificaron la estructura de cada proteína como plegada o desordenada de una manera que coincidía con los resultados experimentales del estudio.
Luego, Liu, Yuan y sus mentores israelíes aplicaron los algoritmos a las proteínas huérfanas “recién nacidas”, que luego fueron purificadas y caracterizadas adecuadamente de manera experimental. Después de buscar en la literatura científica, los científicos identificaron siete de estas proteínas huérfanas cuya función, pero no su estructura, se conocía.
Las herramientas de inteligencia artificial indicaron que cinco de los siete estaban plegados de forma compacta, mientras que dos parecían carecer de una estructura definida. Para uno de los cinco, los tres algoritmos hicieron predicciones sorprendentemente similares, lo que indica una probabilidad de precisión muy alta, hasta el punto de que la revista mostró las tres estructuras 3D en su portada.
Además, los científicos buscaron en el banco de datos de proteínas y encontraron tres proteínas huérfanas cuyas estructuras cristalinas se determinaron experimentalmente. Sorprendentemente, dos de estas proteínas mostraron pliegues que no se sabe que existan en otros lugares. Dado que la estructura determina la función de las proteínas, los nuevos pliegues sugieren que algunas proteínas huérfanas pueden realizar funciones biológicas previamente desconocidas que podrían explotarse en el futuro para una variedad de aplicaciones útiles, desde cortar plástico hasta generar energía limpia o tratar enfermedades.
«Esta investigación cambia nuestra idea de cómo funciona la evolución», dice Sussman. «La evolución generalmente ocurre de la manera que describió Darwin, pero a veces las proteínas pueden aparecer, en cierto sentido, de la nada. Por lo tanto, pueden aparecer nuevos rasgos a partir de en ninguna parte, por así decirlo, «en lugar de haber evolucionado a partir de ancestros durante millones de años». Sillman añade que los hallazgos del estudio, junto con otros estudios sobre proteínas «nacientes», están cambiando la forma de pensar sobre el origen de la vida en general, y de los humanos en particular: «Parece como si no fuéramos simplemente descendientes de E. coli».
«Esperamos que nuestro estudio motive a otros científicos a examinar proteínas huérfanas utilizando herramientas de predicción de IA para tener una idea de su estructura y función», concluye Sussman, «y cuando emerge una estructura completamente nueva, todas las apuestas están descartadas en cuanto a qué La proteína podría funcionar bioquímicamente”. . Aquí es cuando se abren nuevos y apasionantes horizontes de investigación”.
Liu ahora está estudiando su maestría en el laboratorio del profesor Nima Barkai en el Departamento de Genética Molecular de Weizmann, y Yuan es actualmente un estudiante de posgrado en el Centro Médico Southwestern de la Universidad de Texas en Dallas. El profesor Sussman trabaja en el Departamento de Biología Química y Estructural de Weizmann, el profesor Silman en el Departamento de Ciencias del Cerebro y el profesor Pinghai Yan en el Departamento de Física de la Materia Condensada. El profesor Amit Winkler, del Departamento de Física Química y Biológica, coordina el Programa YutChun-Weizmann en la Facultad de Química.
El Programa YutChun-Weizmann es parte de una iniciativa destinada a fortalecer la cooperación académica entre China y la comunidad científica internacional. Entre sus actividades, el programa brinda oportunidades de investigación a destacados estudiantes universitarios.
más información:
Jing Liu et al., ¿Son las proteínas huérfanas “recién nacidas” similares a las proteínas “nunca nacidas”? Un estudio que utiliza tres algoritmos de aprendizaje profundo, Proteínas: estructura, función y bioinformática. (2023). doi: 10.1002/prot.26496

«Solucionador de problemas. Gurú de los zombis. Entusiasta de Internet. Defensor de los viajes sin disculpas. Organizador. Lector. Aficionado al alcohol».